RNA messaggero
Che cos'è l'RNA messaggero?
L'RNA messaggero, abbreviato con mRNA, è costituito da un filamento di ribonucleotidi ed ha la funzione di trasportare l'informazione genetica dal DNA nucleare al citoplasma per la sintesi delle proteine.
Nel DNA infatti è contenuta l'informazione genetica per la produzione delle proteine necessarie per la struttura e le funzioni biologiche di ciascun tipo di cellula sia essa procariote o eucariote.
Il processo mediante il quale l'RNA messaggero è sintetizzato a partire da un'elica di DNA che funge da stampo, prende il nome di trascrizione e ne è responsabile un enzima che si chiama RNA polimerasi (vedi di seguito).
L'RNA messaggero è codificato a partire da un'elica di DNA che funge da stampo ed è quindi complementare ad essa ma ha di conseguenza la stessa sequenza di nucleotidi del filamento codificante (che è il complementare dello stampo).
L'mRNA ha un'emivita breve nella cellula.
Struttura dell'RNA messaggero
L'mRNA è un acido nucleico e come tale è un polimero dei monomeri detti ribonucleotidi.
Si tratta di strutture costituite da uno zucchero a 5 atomi di carbonio, il ribosio, una base azotata (chimicamente la base azotata è una struttura eterociclica con atomi di azoto oltre che di carbonio) ed uno o più gruppi fosfato.
Il ribosio è legato alla base azotata tramite un legame N-glicosidico tra il gruppo OH in posizione 1 del ribosio (detta posizione 1' per distinguerla dalle posizioni della base azotata) e l'atomo di azoto della base azotata.
La posizione 5' del ribosio lega invece il o i gruppi fosfato con legame estere (tra l'OH in posizione 5' del ribosio e l'acido fosforico).
Le basi azotate presenti nell'mRNA sono: adenina, guanina (purine) e citosina ed uracile (pirimidine), come in tutti gli RNA, la timina del DNA è qui sostituita dall'uracile.
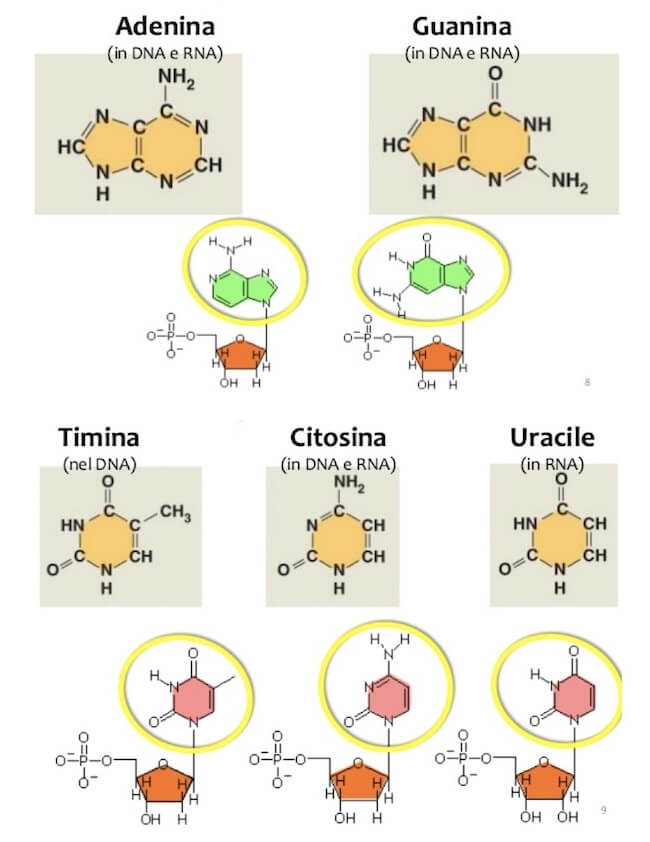
Nucleotidi: purine (in alto) e pirimidina (in basso).
È possibile naturalmente rispettare la complementarietà delle basi anche per quanto concerne il messaggero che, come vedremo viene sintetizzato a partire da un'elica del DNA che funge da stampo, proprio grazie alla complementarietà delle basi azotate: la guanina lega la citosina, l'adenina l'uracile.
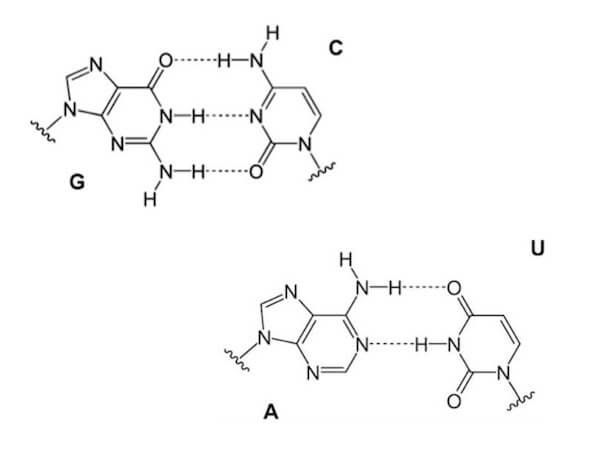
Complementarietà nell'RNA: gli appaiamenti avvengono tra guanina (G) e citosina (C) e tra adenina (A) e uracile (U).
La trascrizione del DNA
L'enzima responsabile di questo processo che in sostanza è simile in tutti gli organismi, dai batteri all'uomo, è l'RNA polimerasi.
Anche l'enzima, come il processo, è molto conservato negli organismi, nel senso che le RNA polimerasi batteriche ed eucariotiche sono simili specie nella subunità dell'enzima più direttamente coinvolta nella catalisi della sintesi dell'RNA.
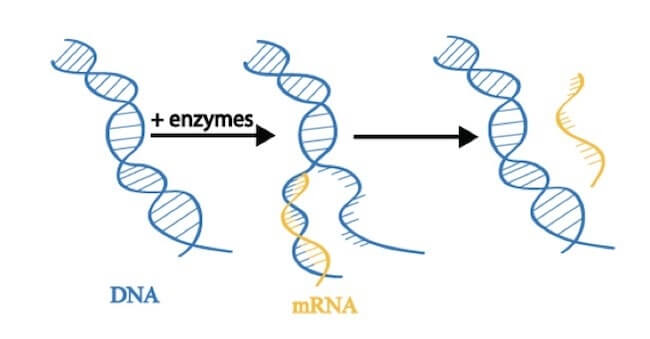
Il processo della trascrizione.
Una delle caratteristiche comuni delle RNA polimerasi, che le differenzia per altro dalle DNA polimerasi (enzimi che si occupano della duplicazione del DNA della cellula prima della divisione cellulare e dunque sintetizzano una nuova elica di DNA utilizzando DNA come stampo) è che sono in grado di sintetizzare RNA senza un primer (piccolo oligonucleotide, complementare al filamento stampo, che innesca la sintesi di un nuovo filamento) , possono iniziare dunque la trascrizione ex novo.
Il processo di trascrizione e soprattutto la maturazione dell'elica di RNA dopo la trascrizione, presentano tuttavia delle differenze tra Procarioti ed Eucarioti.
Nei Procarioti è presente un solo tipo di RNA polimerasi, la trascrizione segue le fasi di inizio, allungamento e termine, come negli Eucarioti ma sono differenti le sequenze promotori e le proteine coinvolte nella sintesi (vedi Trascrizione).
La molecola che viene sintetizzata è un lungo filamento di RNA messaggero che è definito policistronico, ovvero codifica per più proteine, contiene l'informazione di più geni.
Inoltre poiché nei batteri non vi è un nucleo l'mRNA può cominciare ad essere tradotto in proteine prima che sia terminato il processo di trascrizione.
I geni policistronici spesso appartengono a vie metaboliche comuni, ovvero proteine che intervengono nella stessa via metabolica batterica, sono sintetizzati a partire da geni codificanti per esse che si trovano vicini sul cromosoma batterico, si parla di operoni.
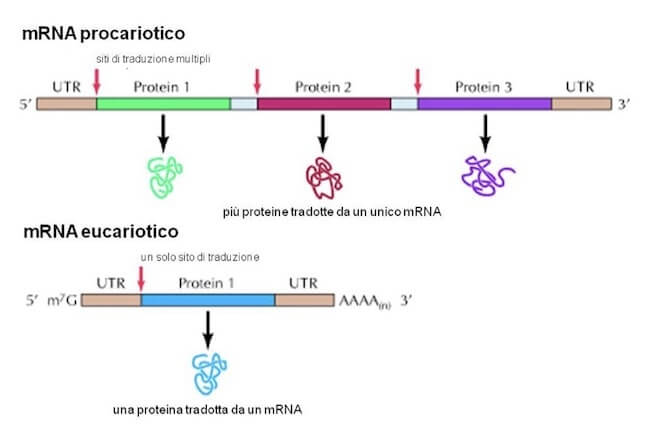
Differenze nella traduzione dell'mRNA in Procarioti ed Eucarioti.
Negli Eucarioti sono presenti 3 diverse RNA polimerasi, la RNA polimerasi I, la II e la III.
La Pol II è l'enzima di cui ci occupiamo qui poiché è responsabile della trascrizione di quasi tutti i geni o meglio di tutti i geni che codificano per delle proteine.
La Pol I trascrive i geni per gli RNA ribosomiali, mentre la Pol III trascrive i geni per i tRNA e per l'RNA ribosomiale 5S (oltre ad alcuni snRNA, small nuclear).
Gli mRNA eucariotici contengono sequenze codificanti per un solo gene, sono quindi definiti monocistronici, inoltre rappresentano il prodotto della maturazione dei trascritti primari.
I trascritti primari sono il risultato della sintesi da parte della RNA polimerasi II eucaristica.
Questo trascritto primario deve subire tre importanti processi di maturazione per dare luogo al vero e proprio mRNA maturo che possa uscire dal nucleo ed essere tradotto in proteina nel citosol ad opera dei ribosomi.
Il processo di maturazione dei messaggeri eucarioti include tre fasi:
- aggiunta di un cap al 5': capping;
- rimozione degli introni mediante splicing;
- aggiunta di una coda di poliA (poliadenilazione) al 3'.
Il capping consiste nell'aggiunta di una 7metil Guanina (/mG) all'estremità del trascritto con un particolare legame 5'-5' (normalmente i nucleotidi si legano con legame 3-5'). L'aggiunta del cap avviene quando l'RNA è lungo 20-40 nucleotidi, quindi poco dopo l'inizio del processo di trascrizione.
La sequenza codificante di un gene è una serie di codoni (tre nucleotidi) che specificano la sequenza lineare degli amminoacidi del suo prodotto polipeptidico.
Finora, abbiamo implicitamente assunto che la sequenza codificante sia continua ovvero che il codone per un amminoacido sia immediatamente adiacente al codone per l'amminoacido successivo del polipeptide.
Se ciò è vero nei Procarioti non lo è invece negli Eucarioti, in essi infatti la sequenza codificante è interrotta periodicamente da segmenti di sequenza non codificante.
Dunque i geni eucariotici sono dei mosaici, cioè sono costituiti da blocchi di sequenze codificanti separati gli uni dagli altri da blocchi di sequenze non codificanti. Le sequenze codificanti sono chiamate esoni, mentre quelle interposte non codificanti sono definite introni.
Poiché solo gli esoni codificano per le proteine, le sequenze introni che devono essere rimosse nella fase della maturazione dell'mRNA eucaristico che prende il nome di splicing (i geni che hanno queste interruzioni non codificanti sono detti "divisi" o "split") ed avviene ad opera di enzimi specializzati che riconoscono le estremità degli esoni, taglaino gli introni e legano tra loro le parti codificanti nel corretto ordine per ottenere una sequenza unica codificante la proteina.
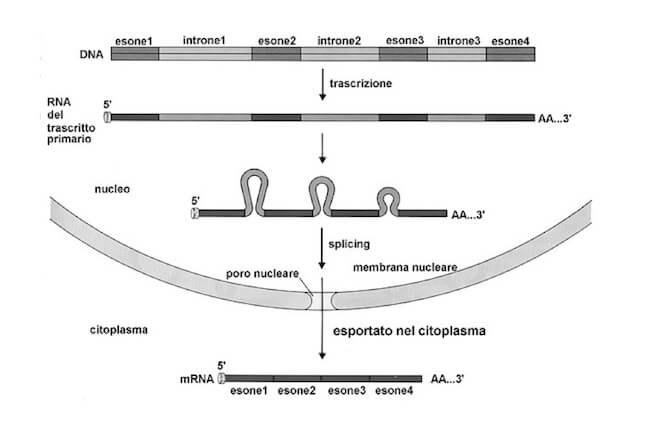
Lo splicing: la rimozione delle sequenze non codificanti, gli introni.
La coda di poly A (di circa 250 nucleotidi) è aggiunta dopo la trascrizione da un enzima chiamato Poly A polimerasi che aggiunge residui di AMP, uno alla volta al trascritto primario.
La poliadenilazione ha due funzioni:
- aumenta la vita media del mRNA dunque ha una funzione protettiva (dalla degradazione ad opera di enzimi litici);
- consente la traduzione dato che una delle proteine che si lega agli mRNA durante la traduzione è la proteina I che ha come sito di riconoscimento proprio il poly A.
Il legame a questa proteina aumentare l'efficienza con cui è tradotto l'mRNA.
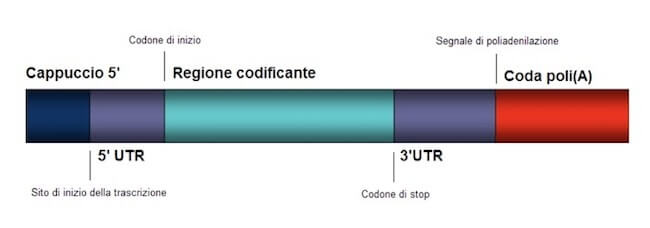
Schema di un mRNA maturo eucariotico.
Link correlati:
Qual è la differenza tra DNA e RNA?
Studia con noi